吉林大学人工智能学院2021级博士研究生范毅在导师李向涛教授指导下,在单细胞多组学数据整合研究方面取得重要进展,提出了一种新的整合方法 OmiDos。该方法从“信号解耦”的角度出发,为复杂生物系统调控网络的联合解析提供了新的计算框架。与传统方法将不同模态信息直接压缩到统一潜在空间的做法不同,OmiDos 显式地区分并学习两类表示:一类用于刻画组学特异性特征,另一类用于捕捉跨组学的协同调控信息。通过这种“正交解耦”的设计,模型在保留各组学层独特信息的同时,能够更准确地提取具有生物学意义的共享调控程序。相关成果以“Orthogonal disentanglement of single-cell multi-omics reveals private and shared drivers of tissue development and pathogenesis” 为题发表在国际学术期刊Proceedings of the National Academy of Sciences(PNAS)。

范毅,吉林大学人工智能学院2021级博士生,重点关注深度无监督学习的单细胞多组学数据整合与聚类方法,并探索其在细胞发育与疾病机制研究中的应用,围绕基因调控、多组学整合等相关问题开展系统研究。相关成果发表于PNAS、Advanced Science、Bioinformatics等期刊。
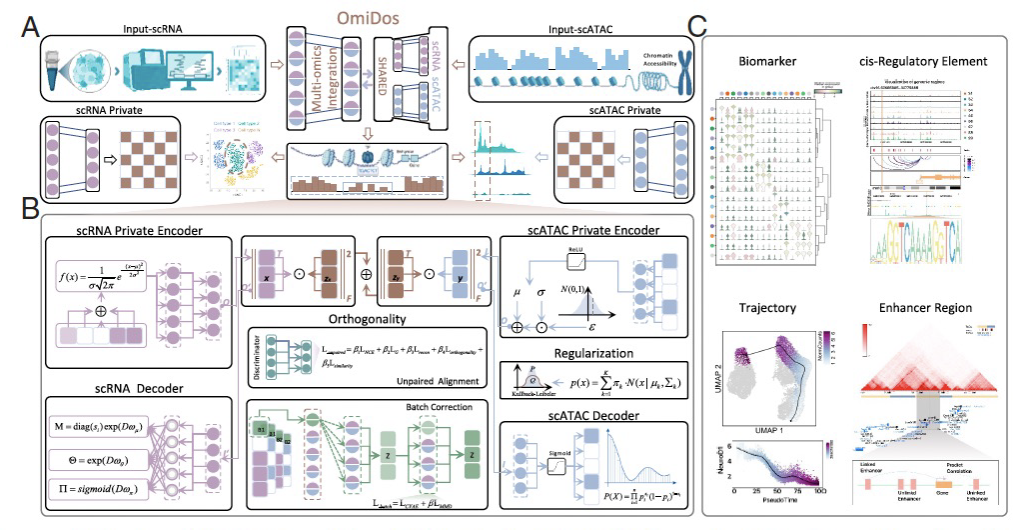
表征正常组织功能与疾病进展背后的基因表达及调控动态,需要对单细胞多组学数据进行整合分析。然而,基因调控的异步性以及单细胞多组学数据的瞬时快照特性,会产生各组学层面特有的独立信号,同时也存在反映跨模态协同作用的共享信号。研究提出一种基于域自适应的组学分离建模方法(OmiDos),这是一个无需注释、灵活通用的深度学习框架,通过独立--共享成分分析,在多组学数据中解耦组学特异性与组学间共享的潜在变量。其模块化架构支持无缝扩展,可引入对抗学习以处理非配对数据的错位问题,并通过重构组件利用最大均值差异正则化,从而最小化对生物异质性的干扰。借助这种解耦机制,OmiDos能够在更精细的生物尺度上解析基因表达与调控动态,并支持多种下游分析。在不同平台、不同组织类型的多个数据集上验证了OmiDos在聚类精度、批次效应校正及数据错位校正方面的优越性能。在小鼠次生腭发育研究中,OmiDos精准识别出一种细胞类型特异性的非连锁远端增强子,阐明了其在上皮细胞分化与迁移调控中的关键作用。将OmiDos应用于髓母细胞瘤研究后发现,Neurod1基因远端增强子区域部分闭合过程中可能存在调控功能缺陷,这或许是髓母细胞瘤从正常状态向肿瘤状态进展的重要诱因。
原文链接:https://www.pnas.org/doi/10.1073/pnas.2519870123
